por Héctor Romo-Parra
Durante décadas, la biología ha perseguido una pregunta que suena a ciencia ficción, pero que en realidad es profundamente práctica: ¿podemos simular por completo una célula viva en una computadora?
Hoy esa idea está un poco menos lejos.
quédate
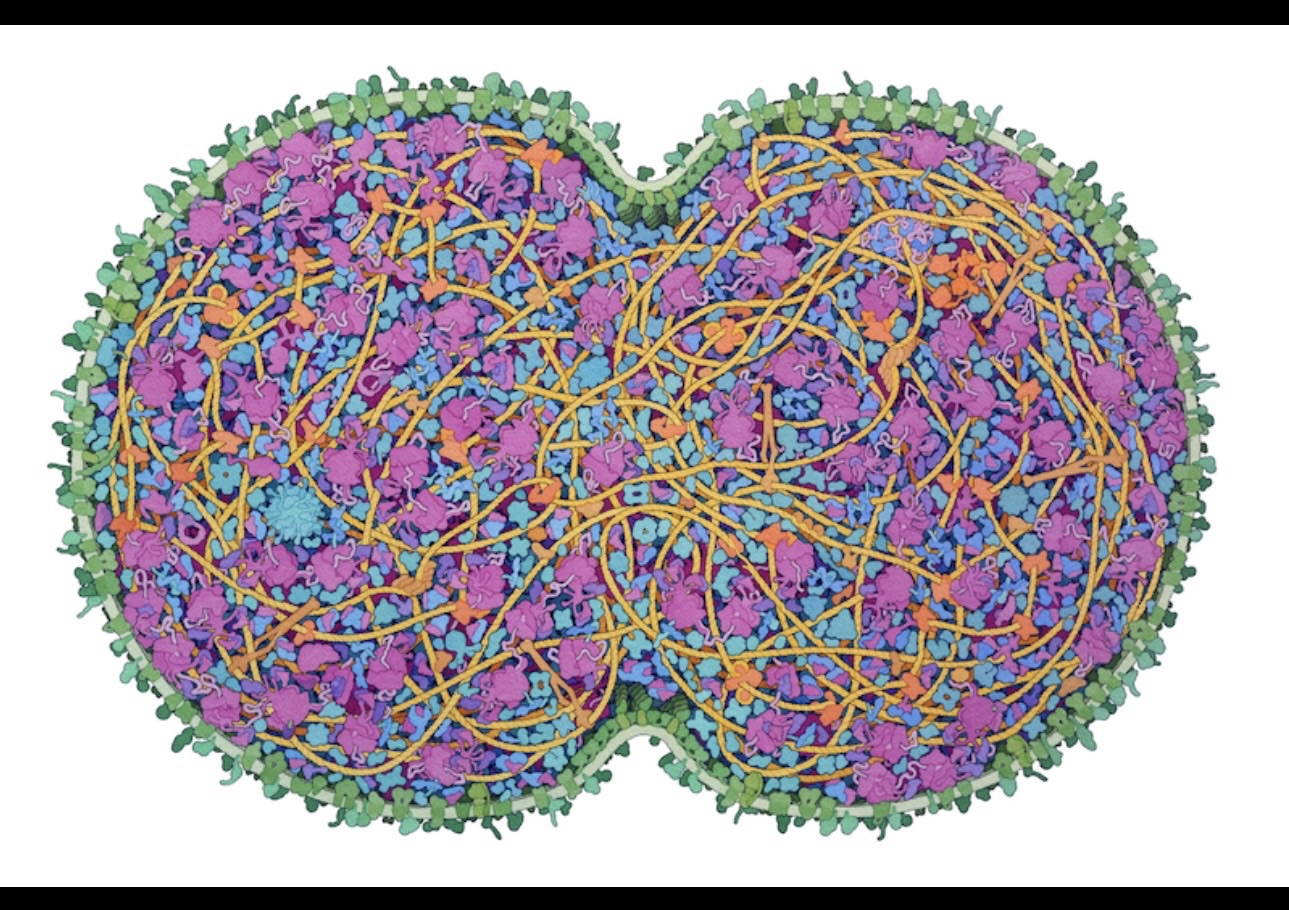
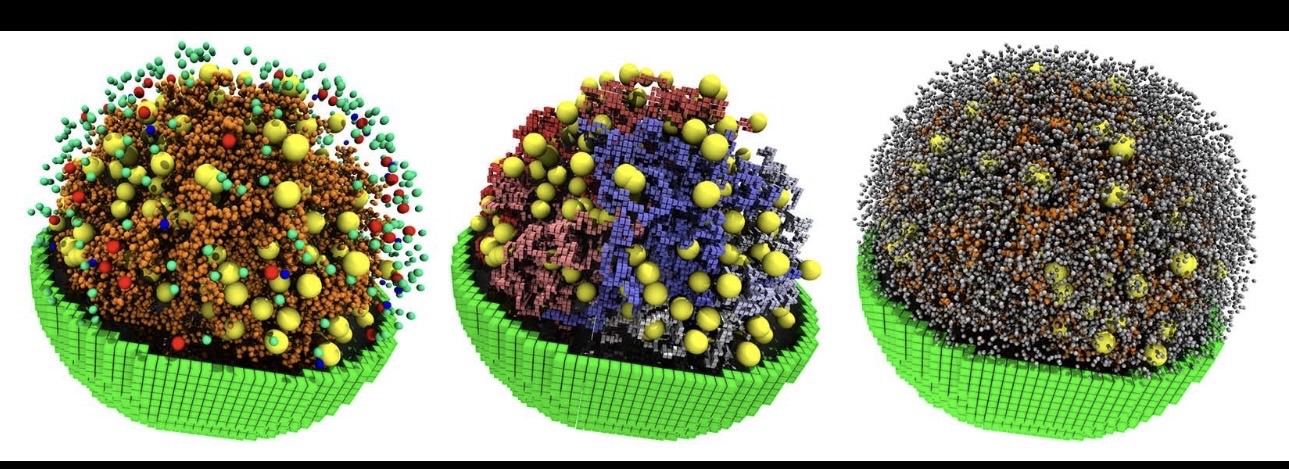
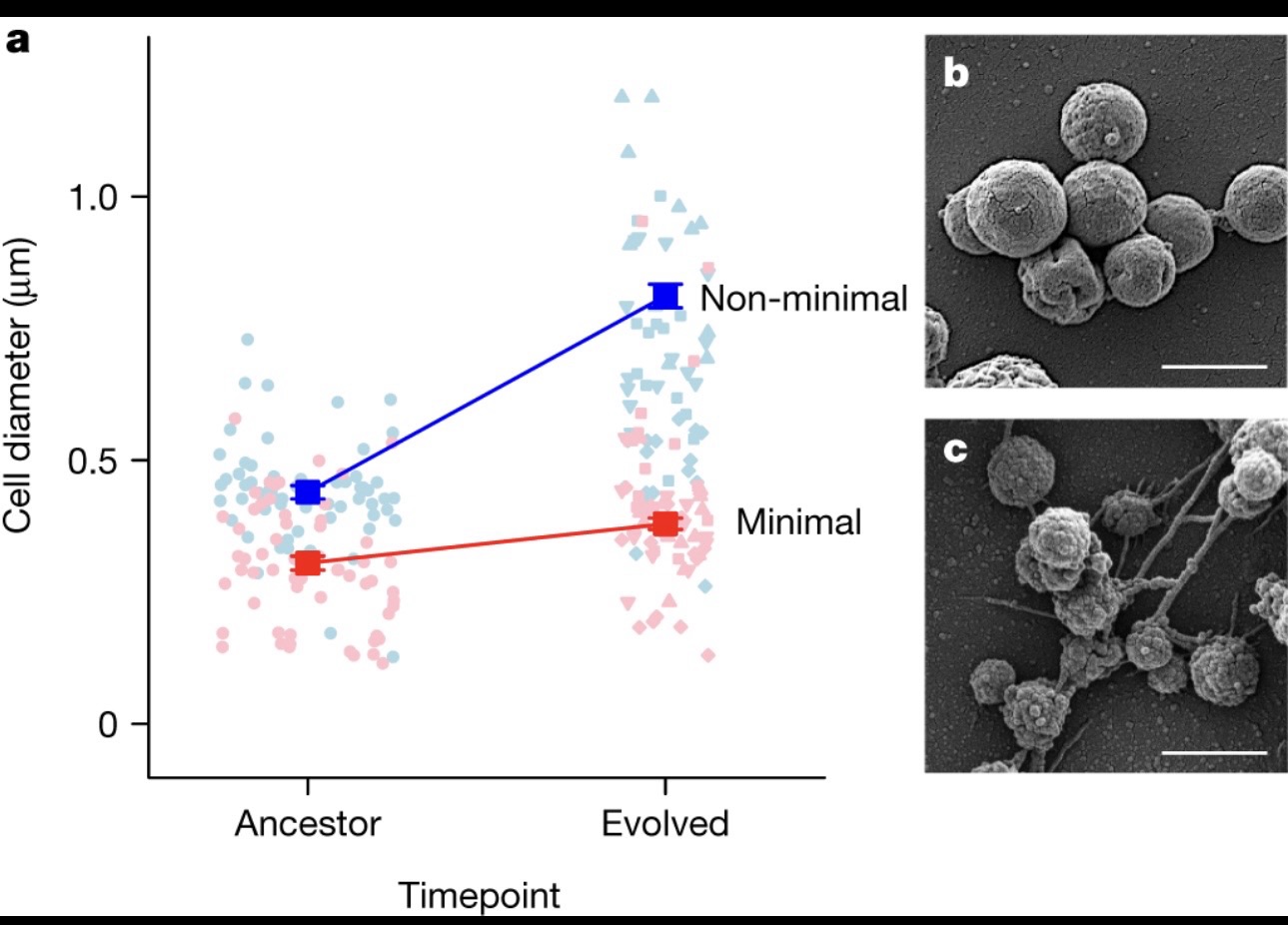
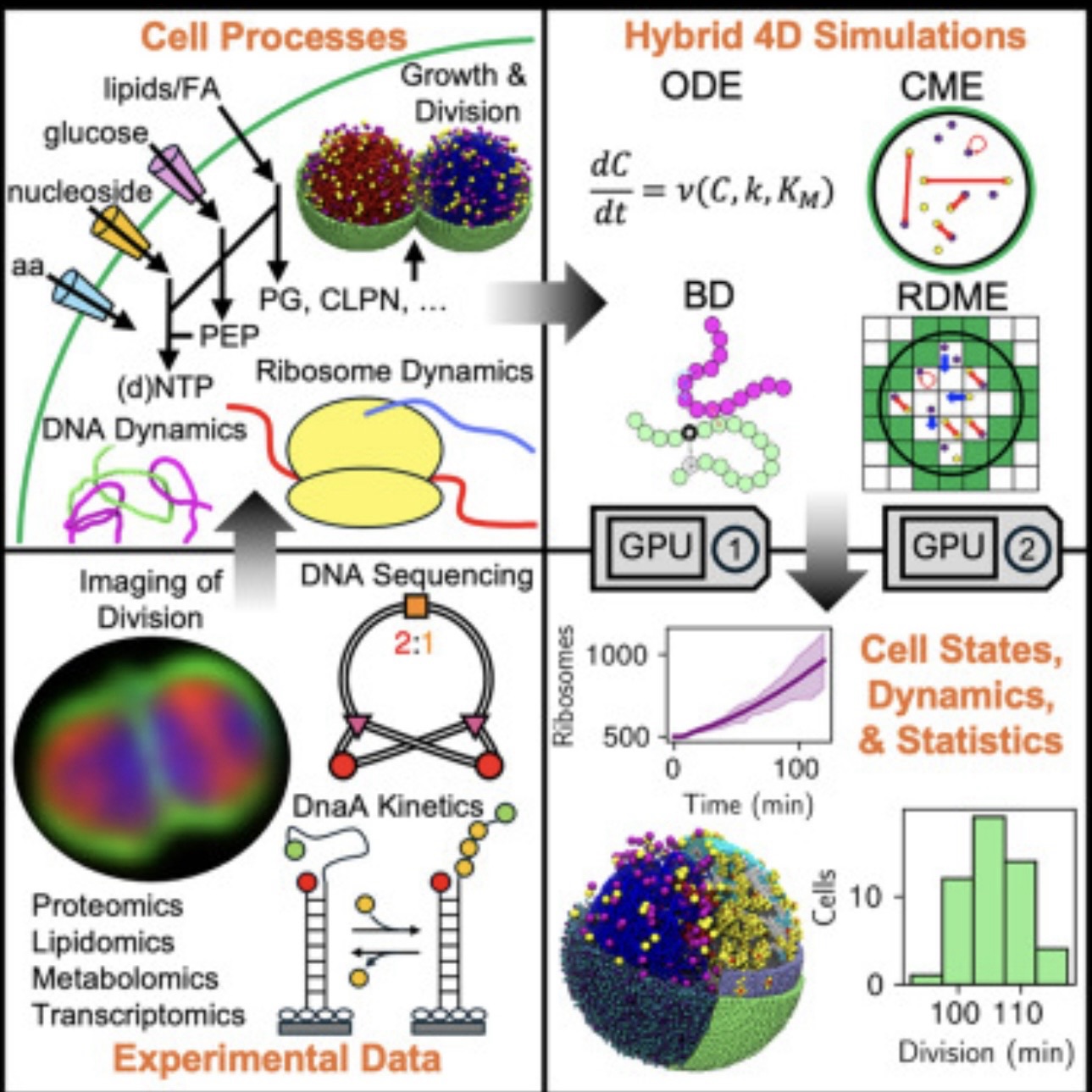
imágenes tomada del articulo original (ver referencias)
Un equipo de investigadores presentó en Cell un modelo que intenta recrear, de forma integrada, todo el ciclo de vida de una bacteria sintética llamada JCVI-syn3A, un organismo desarrollado por el J. Craig Venter Institute para estudiar qué es lo mínimo necesario para sostener la vida.
Lo asombroso de JCVI-syn3A es su simplicidad genética: 493 genes. Para ponerlo en perspectiva, una célula humana tiene alrededor de 20,000 genes. Esa “minimalidad” la convierte en un laboratorio ideal para algo extremadamente ambicioso: construir una célula virtual que no solo “parezca” viva, sino que funcione con reglas físico-químicas y biológicas coherentes.
Una célula virtual (casi) completa
Lo que distingue a este trabajo es que no se enfoca en un solo proceso, ni en una sola vía.
El modelo simula de manera conjunta, durante un ciclo celular de ~100–105 minutos, procesos esenciales como:
- Replicación del ADN
- Transcripción y traducción
- Biogénesis y actividad de ribosomas
- Metabolismo
- Crecimiento y división celular
Además, el modelo es espacial. No se asume que “todo está perfectamente mezclado” dentro de la célula. Se intenta representar cómo se mueven y reaccionan moléculas en el espacio celular a lo largo del tiempo.
En palabras simples: no es solo un diagrama de rutas metabólicas o una lista de reacciones. Es un intento de “poner a correr” una célula minimalista dentro de una simulación 4D (espacio + tiempo).
El costo computacional de simular la vida
Este logro también deja clara una verdad incómoda: simular biología realista es carísimo.
Para simular un solo ciclo celular, el equipo reporta que se requiere:
- 4 a 6 días de cómputo en GPUs (por célula simulada)
- una velocidad de simulación ~80 veces más lenta que el tiempo real de la célula
- cerca de 15,000 horas de GPU para simular 50 ciclos celulares
Aunque JCVI-syn3A es “minimalista”, la vida no se reduce linealmente. Incluso con menos genes, sigue existiendo una red enorme de interacciones, dependencias y retroalimentaciones.
¿Por qué importa?
Este tipo de modelos abre puertas muy interesantes:
- probar in silico los efectos de mutaciones antes de ir al laboratorio
- estudiar fallas de sistemas biológicos como “problemas de dinámica” (no solo de piezas)
- diseñar organismos sintéticos con objetivos específicos
- avanzar hacia gemelos digitales celulares para explorar respuestas a fármacos
Al mismo tiempo, hay que ser honestos: estamos muy lejos de simular una célula humana completa.
La complejidad biológica no solo aumenta con el número de genes. Aumenta por la cantidad de posibles interacciones y contextos, que crece de manera combinatoria.
Aun así, este trabajo marca un punto de inflexión.
Por primera vez, la biología se acerca con seriedad a una idea que hace poco parecía imposible: tener organismos “funcionando” dentro de un modelo computacional, y no solo descritos por datos.
Referencias
- Thornburg, Z. R., Maytin, A., Kwon, J., et al. (2026). Bringing the genetically minimal cell to life on a computer in 4D. Cell. https://doi.org/10.1016/j.cell.2026.02.009
- Hutchison, C. A., Chuang, R.-Y., Noskov, V. N., et al. (2016). Design and synthesis of a minimal bacterial genome. Science, 351(6280), aad6253.
- Karr, J. R., Sanghvi, J. C., Macklin, D. N., et al. (2012). A whole-cell computational model predicts phenotype from genotype. Cell, 150(2), 389–401. https://doi.org/10.1016/j.cell.2012.05.044

Deja un comentario